Responsables
Guillaume Velasco – Olivier Kirsh
Guillaume Velasco – Olivier Kirsh
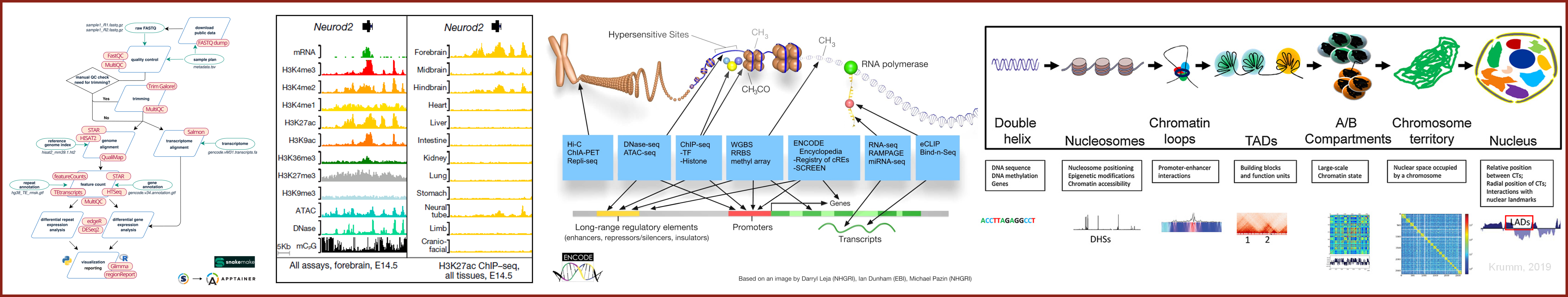
Aborder les aspects fondamentaux du rôle l’épigénome et de ses bases moléculaires sur la régulation du génome ainsi que les méthodes expérimentales et analyses bio-informatiques utilisées dans ces différents aspects. L’analyse des données omiques sera spécifiquement abordée sous la forme de TD/TP mêlant savoir et savoir/faire
Epigénome et omics : régulation transcriptionnelle
Infrastructure bioinfo, outils et workflow
Structure et organisation 3D du génome
Marques épigénétiques et compartiments chromatiniens
Méthylation de l’ADN
Expression monoallèlique : empreinte parentale et inactivation du chromosome X
Epigénome et intégrité du génome
Répartition de l’UE sur 12 semaines. Chaque thème est abordé sur 2 semaines : une semaine est dédiée aux concepts abordés en CM et TD. L’autre semaine est consacrée aux aspects savoir-faire en TP avec ordinateur.
70% orale 30% écrit : La note est basée sur une évaluation orale de 15 minutes et un rapport écrit présentant les résultats d’analyses omics effectuées dans le cadre d’un mini projet.